标签:mat 下载 网站 oca -- 不用 exist -o 后缀
老师要做一个关于生物信息工程的网站,一个同学要负责网站的搭建,让我来研究blast。但是这个软件的教程太少了,在看的过程中走了不少弯路。写个文章记录一下,以便以后使用。同时还会根据项目的进程进行更新。 ---2019/10/24
一、说明
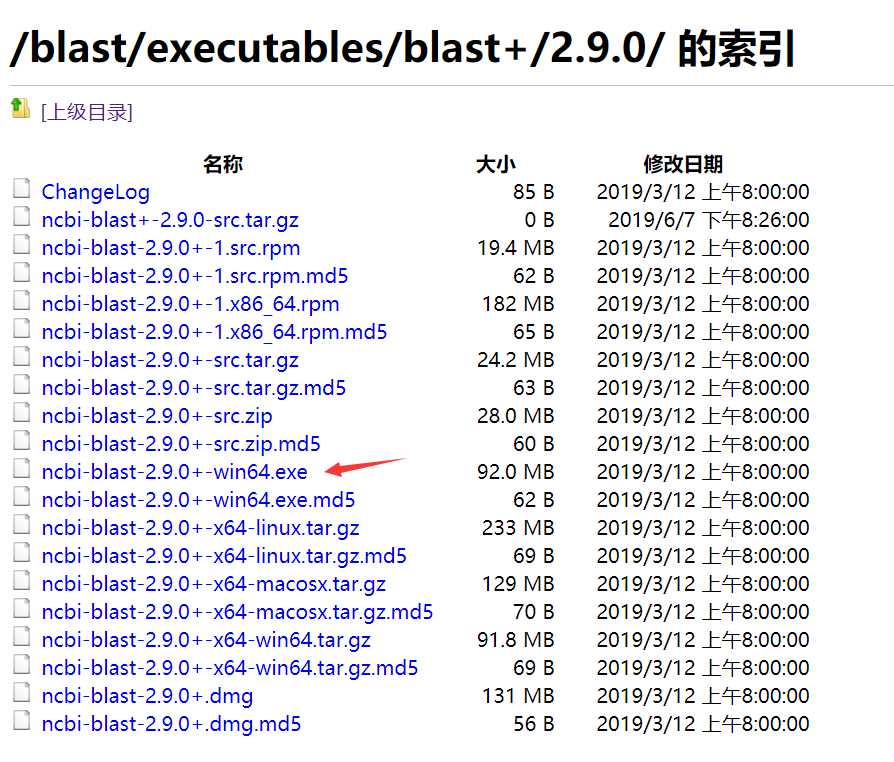
下载红箭头指向的文件
下载之后发现文件结果如下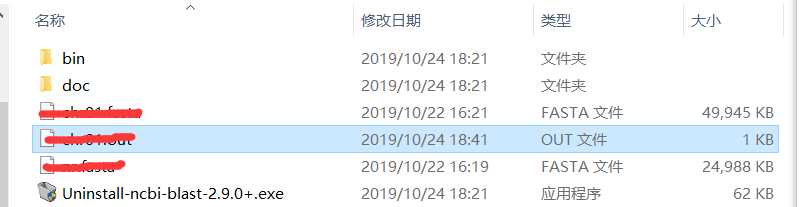
一个bin,一个doc,一个卸载程序,但是点开bin之后就懵了。bin中几乎一半都是exe文件,但是这些exe文件没有一个是打开这个程序的,都只是些命令程序。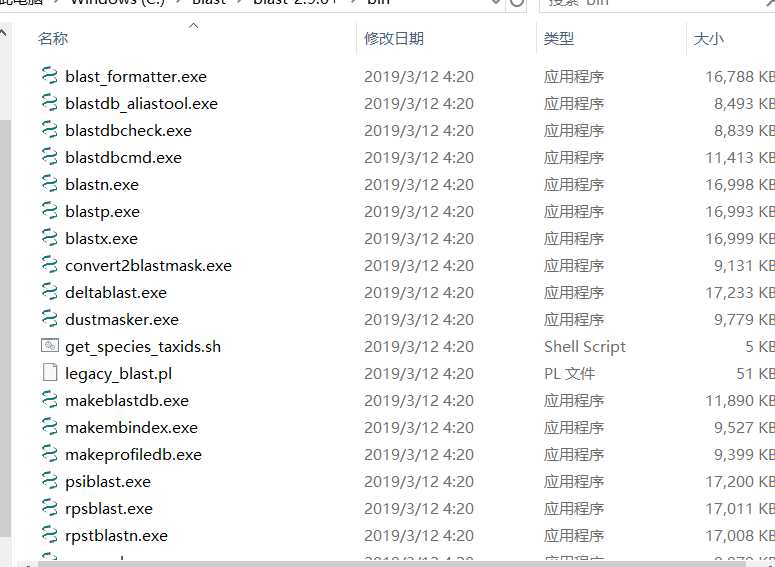
因为没办法直接使用,因此只能去cmd中用命令调用。
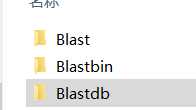
2.1在c盘下建立三个包
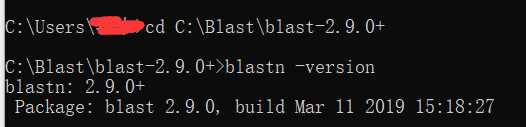
移动到blast有bin的包下,输入blastn -version来看是否安装成功
2.2创建db
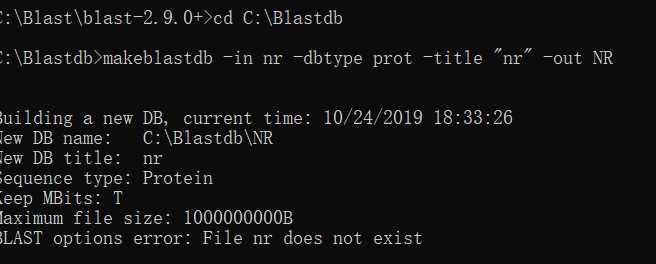
这个最后一个出问题了,它提示我File nr does not exist,然而我的nr文件是存在的。后来发现nr必须有文件后缀。(nr.fasta是要建成数据库的文件)
(建库命令:makeblastdb -in nr.fasta -dbtype prot -title "nr" -out NR)
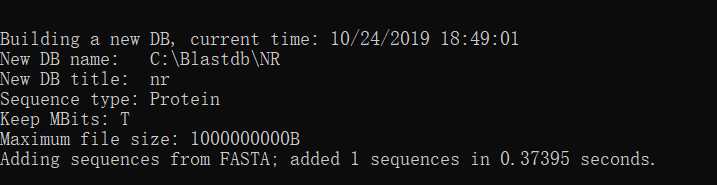
2.3建好库后测试
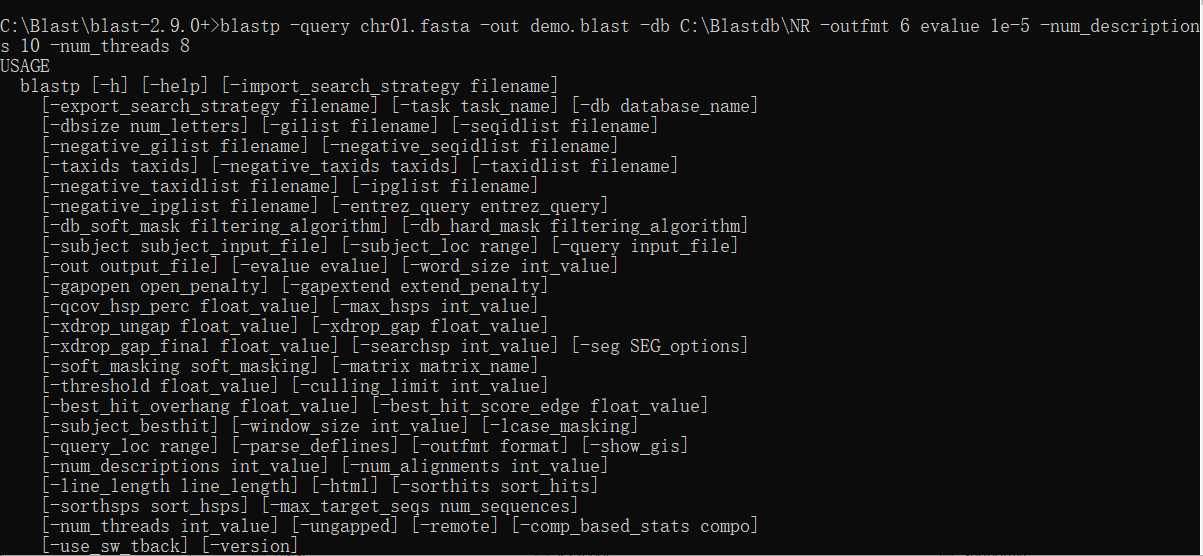
到这一步基本上在win下已经能够正常的调用blast来运行代码了。这些处理结果和输入参数看不明白,也不用看明白。
三、常用的blast命令
二、格式化数据库
基本运行指令
formatdb -i DBfile1 -p (T/F) -o (T/F)
-i:输入需要格式化序列库的绝对路径,序列库一般一般使用的是fasta文件。
-o [T/F]:判断是否分析序列名并建立序列名索引。“T”表示建立序列名索引,“F” 表示不建立序列名索引。默认值为F。
-p [T/F]:选择建库的类型,“T”表示建立的是蛋白质数据库,“F”表示建立的是核酸数据库,缺省值为T。
java代码
Process process = Runtime.getRuntime.eexec("formatdb -i DBFile -p T -o T");
process.waitFor(); //等待命令执行结束,获取执行结果
程序运行结束后,如果建立的是核酸库,-o为F时,会输出**.nhr,**.nin,**.nsp文件,-o为T时,还会多输出**.hsd,**.nsi,**.nni和**.nnd文件。类似的,当建立的是蛋白质也会输出相应的文件:[-o F]--**.phr,**.pin,**.psq;[-o T]--**.psd,**.psi,**.pni,**.pnd。
三、在数据库中查询相应序列并返回结果
1.基本运行指令:blastall -i query.fasta -d database_prefix -o blast.out -p blastn [-e value -F (T/F) -m value -v 500 -b 250 -T (T/F)]
2.blast主程序blastall
程序的输入文件是query序列(-i参数)库文件(-d)
选择(-p)和输出文件(-o)有用户绝定
-p有五种取值:百度查找
3.-e参数
筛选适当的比对结果,指定一个参数,选出比这个参数大的期望值
4. -F (T/F)参数
用来屏蔽简单重复和低复杂度序列的。
T:程序在比对过程中会屏蔽掉query中的简单重复和低复杂度序列
F:不会屏蔽
缺省值(默认值)为“T”。
5.-m参数
设定输出格式,供选择为0~11之间的整数。默认0.
6.-v,-b参数
-v 默认值500,规定输出中的每一个query的比对列表最多显示subject的个数
-b 默认250,规定输出中每个query最多显示与多少subject的比对条形图
7. -T 参数
用于决定是否输出html格式的比对结果。
9.-W参数
指定坐比对的字的长度。
四、java程序中调用blast
....
标签:mat 下载 网站 oca -- 不用 exist -o 后缀
原文地址:https://www.cnblogs.com/mushuise/p/11734281.html